Genetic Research of Sheep-Goats and Cattle in Kazakhstan: A Review of Research in 2025 Генетические исследования овец-коз и крупного рогатого скота в Казахстане: обзор научных работ 2025 года Қазақстандағы қой-ешкі және ірі қара малдарының генетикалық зерттеулері: 2025 жылдағы ғылыми жұмыстарға шолу
Abstract Аннотация Түйіні
This review article analyzes recent molecular genetic and genomic studies conducted on Kazakhstani populations of sheep-goats, and cattle, based on scientific publications indexed in the Scopus database in 2025. The review examines research on genetic diversity, population structure, selection signatures, and genomic associations with economically important traits. Particular attention is given to studies utilizing modern technologies such as SNP genotyping and whole-genome sequencing. The results demonstrate significant achievements in understanding the genetic architecture of Kazakhstani livestock breeds and provide a foundation for implementing genomic selection programs.
В обзорной статье проанализированы современные молекулярно-генетические и геномные исследования, выполненные на казахстанских популяциях овец, коз и крупного рогатого скота (КРС) на основе научных публикаций, индексированных в базе Scopus за 2025 год. Рассматриваются исследования генетического разнообразия, популяционной структуры, следов селекции и геномных ассоциаций с хозяйственно-важными признаками. Особое внимание уделяется работам с применением современных технологий, таких как SNP-генотипирование и полногеномное секвенирование. Результаты демонстрируют значительные достижения в понимании генетической архитектуры казахстанских пород сельскохозяйственных животных и создают основу для внедрения программ геномной селекции.
Бұл шолу мақалада 2025 жылда жарияланған ғылыми еңбектерге негізделе отырып, Қазақстандағы ауыл шаруашылық малдарының генетикалық зерттеулеріне талдау жасалды. Шолуда қой-ешкі және ірі қара малдарының генетикалық әртүрлілігі, популяциялық құрылымы, селекция іздері және шаруашылық маңызды белгілермен геномдық байланыстары қарастырылған. Зерттеулерде SNP-генотиптеу және толық геномды секвенирлеу сияқты заманауи технологиялар қолданылған. Нәтижелер Қазақстандағы ауыл шаруашылық мал тұқымдарының генетикалық архитектурасын түсінуде елеулі жетістіктерді көрсетеді және геномдық селекция бағдарламаларын енгізу үшін негіз жасайды.
Graphical Abstract Графический абстракт Графикалық аңдатпа
Visual summary of the study. Визуальное резюме исследования. Зерттеудің визуалды қысқаша мазмұны.
IntroductionВведениеКіріспе
Livestock farming plays a crucial role in ensuring food security in the Republic of Kazakhstan, sustainable development of the agricultural sector, and preserving the socio-economic potential of rural areas. Local breeds of agricultural animals adapted to harsh continental climate conditions, characterized by high temperature fluctuations and limited feed resources, represent valuable genetic resources. These breeds have formed over centuries through natural and artificial selection under specific environmental conditions and possess unique adaptive characteristics.
In recent years, advanced approaches in molecular genetics and genomics have fundamentally expanded the methodological capabilities for studying agricultural animals. For instance, single nucleotide polymorphism (SNP) genotyping and whole-genome sequencing (WGS) technologies enable comprehensive analysis of genetic diversity, identification of selection signatures, detection of genomic associations with economically important traits, and assessment of inbreeding levels.
Therefore, the purpose of this article is to provide a comprehensive review of the current state and development trends of genetic research on livestock in Kazakhstan, based on publications in scientific journals indexed in the Scopus database published in 2025. Special attention will be given to studies of sheep, goats, and cattle populations, which are traditional and economically significant sectors of animal husbandry in the country.
Животноводство играет важнейшую роль в обеспечении продовольственной безопасности Республики Казахстан, устойчивом развитии аграрного сектора и сохранении социально-экономического потенциала сельских регионов. Местные породы сельскохозяйственных животных, адаптированные к суровым условиям континентального климата с высокими температурными перепадами и ограниченными кормовыми ресурсами, представляют собой ценный генетический ресурс. Эти породы формировались на протяжении веков в результате естественного и искусственного отбора в специфических условиях среды и обладают уникальными адаптивными характеристиками.
В последние годы передовые подходы в области молекулярной генетики и геномики коренным образом расширили методические возможности изучения сельскохозяйственных животных. Например, технологии генотипирования однонуклеотидных полиморфизмов (SNP) и полногеномного секвенирования (WGS) позволяют проводить комплексный анализ генетического разнообразия, выявлять следы селекции, обнаруживать геномные ассоциации с хозяйственно важными признаками и оценивать уровни инбридинга.
В связи с этим, целью данной статьи является всесторонний обзор современного состояния и тенденций развития генетических исследований животноводства в Казахстане на основе публикаций в научных журналах, индексированных в базе Scopus, опубликованных в 2025 году. Особое внимание будет уделено исследованиям популяций овец, коз и крупного рогатого скота, которые являются традиционными и экономически значимыми отраслями животноводства в стране.
Ауыл шаруашылық малдары Қазақстан Республикасының азық-түлік қауіпсіздігін қамтамасыз етуде, аграрлық сектордың тұрақты дамуында және ауылдық аймақтардың әлеуметтік-экономикалық әлеуетін сақтауда маңызды рөл атқарады. Континенталды климаттың қатал жағдайларына, жоғары температуралық ауытқуларға және шектеулі жем ресурстарына бейімделген жергілікті ауыл шаруашылық мал тұқымдары құнды генетикалық ресурс болып табылады. Бұл тұқымдар ғасырлар бойы арнайы қоршаған орта жағдайларында табиғи және жасанды іріктеу нәтижесінде қалыптасқан және бірегей бейімделу сипаттамаларына ие.
Соңғы жылдары молекулалық генетика және геномика салаларында қолданылатын жоғары деңгейдегі тәсілдер ауыл шаруашылық жануарларын зерттеудің әдістемелік мүмкіндіктерін түбегейлі кеңейтті. Мысалы, бірнуклеотидті полиморфизмдерді (SNP) генотиптеу және толық геномды секвенирлеу (WGS) технологиялары генетикалық әртүрлілікті кешенді талдауға, селекция іздерін анықтауға, шаруашылық маңызды белгілермен геномдық байланыстарды табуға және инбридинг деңгейін бағалауға мүмкіндік береді.
Осыған орай, бұл мақаланың мақсаты соңғы 2025 жылда жарияланған, Scopus дерекқорында индекстелген ғылыми журналдардағы жарияланымдарға сүйене отырып, Қазақстандағы ауыл шаруашылық малдарының генетикалық зерттеулерінің қазіргі жағдайы мен даму үрдістеріне жан-жақты шолу жасау болып табылады. Елдегі дәстүрлі және экономикалық маңызды мал шаруашылығы салалары болып табылатын қой, ешкі және ірі қара малдардың популяцияларын зерттеуге ерекше көңіл бөлінеді.
I. Genetic Research on Sheep and Goats І. Генетические исследования овец и коз І. Қой және ешкі шаруашылығы бойынша генетикалық зерттеулер
Sheep farming is one of Kazakhstan's traditional and economically important sectors. The fat-tailed coarse-wooled sheep breeds widely distributed in the country have formed under long-term selection in specific environmental conditions and possess unique adaptive characteristics.
A comparative analysis of the genetic structure of fat-tailed coarse-wooled sheep breeds by Dossybayev et al. (2025) aimed to study the genetic characteristics of local fat-tailed coarse-wooled sheep populations in Kazakhstan using modern genomic technologies [1]. The study used SNP genotyping data from 501 samples representing three main Kazakhstani sheep breeds: Kazakh fat-tailed coarse-wool (n=497), Edilbay (n=2), and Hissar (n=2).
Овцеводство является одной из традиционных и экономически важных отраслей Казахстана. Широко распространенные в стране курдючные грубошерстные породы овец сформировались в условиях длительной селекции в специфических условиях окружающей среды и обладают уникальными адаптивными характеристиками.
Сравнительный анализ генетической структуры курдючных грубошерстных пород овец, проведенный Досыбаевым и соавторами (2025), был направлен на изучение генетических особенностей местных популяций курдючных грубошерстных овец Казахстана с использованием современных геномных технологий [1]. В исследовании использовались данные SNP-генотипирования 501 образца, представляющих три основные казахстанские породы овец: казахскую курдючную грубошерстную (n=497), эдильбаевскую (n=2) и гиссарскую (n=2).
Қой шаруашылығы Қазақстанның дәстүрлі әрі экономикалық тұрғыдан маңызды салаларының бірі болып табылады. Елімізде кең таралған қылшық жүнді құйрықты қой тұқымдары ұзақ мерзімді селекцияның нәтижесінде арнайы қоршаған орта жағдайларында қалыптасқан және бірегей бейімделу сипаттамаларына ие.
Қылшық жүнді құйрықты қой тұқымдарының генетикалық құрылымын салыстырмалы талдау бойынша Досыбаев және басқа да авторлар (2025) жариялаған мақаланың негізгі мақсаты жергілікті қылшық жүнді құйрықты қой популяцияларының генетикалық ерекшеліктерін заманауи геномдық технологиялар арқылы зерттеу болды [1]. Зерттеуде үш негізгі қазақстандық қой тұқымын білдіретін 501 үлгінің SNP-генотиптеу деректері қолданылды: қазақтың құйрықты қылшық жүнді (n=497), еділбай (n=2) және гиссар (n=2).
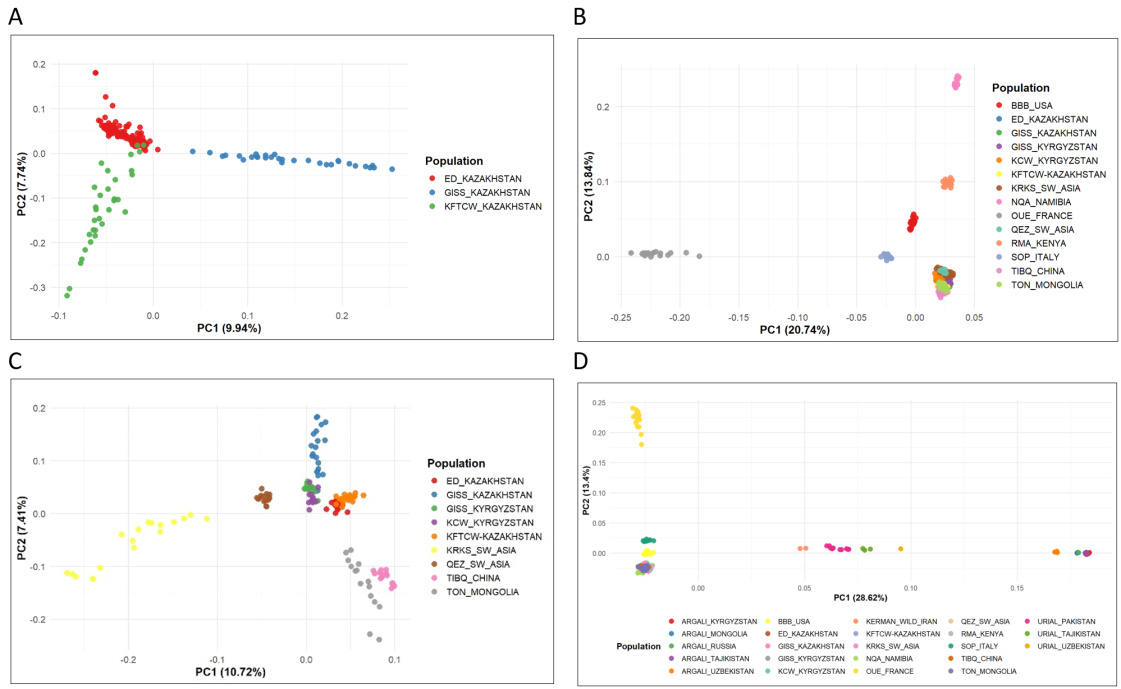
(A) Three studied sheep populations from Kazakhstan. (B) Studied world domestic sheep breeds. (C) Studied Asian domestic sheep breeds. PCA analysis clearly demonstrates the genetic differentiation between the studied breeds. (A) Три изученные популяции овец из Казахстана. (B) Изученные мировые породы домашних овец. (C) Изученные азиатские породы домашних овец. Анализ PCA четко демонстрирует генетическую дифференциацию между изученными породами. (A) Қазақстандағы үш зерттелген қой популяциясы. (B) Зерттелген әлемдік үй қой тұқымдары. (C) Зерттелген азиялық үй қой тұқымдары. PCA талдауы зерттелген тұқымдар арасындағы генетикалық дифференциацияны айқын көрсетеді.
Genomic research results demonstrate the unique genetic identity and high level of genetic diversity of sheep breeds raised in Kazakhstan, particularly the Edilbay breed. The Edilbay breed showed the highest level of genetic diversity (He=0.382), while the Kazakh fat-tailed coarse-wool sheep showed an average level (He=0.359).
Principal component analysis revealed clear differences between Kazakh fat-tailed coarse-wool, Edilbay, and Hissar breeds, indicating that these three sheep breeds, despite phenotypic similarities, have distinct genetic origins and have undergone independent evolutionary paths.
Результаты геномных исследований демонстрируют уникальную генетическую идентичность и высокий уровень генетического разнообразия пород овец, разводимых в Казахстане, особенно породы эдильбай. Порода эдильбай показала наивысший уровень генетического разнообразия (He=0,382), в то время как казахская курдючная грубошерстная овца показала средний уровень (He=0,359).
Анализ главных компонент выявил четкие различия между казахской курдючной грубошерстной, эдильбаевской и гиссарской породами, что указывает на то, что эти три породы овец, несмотря на фенотипические сходства, имеют различное генетическое происхождение и прошли независимые эволюционные пути.
Геномдық зерттеу нәтижелері Қазақстанда өсірілетін қой тұқымдарының, әсіресе еділбай қой тұқымының, айрықша генетикалық бірегейлігі мен жоғары генетикалық әртүрлілік деңгейін көрсетеді. Еділбай тұқымы ең жоғары генетикалық әртүрлілік деңгейін көрсетті (He=0,382), ал қазақтың құйрықты қылшық жүнді қойы орташа деңгейді көрсетті (He=0,359).
Негізгі компоненттерді талдау әдісі арқылы қазақтың қылшық жүнді құйрықты қойы, еділбай және гиссар тұқымдары арасындағы айқын айырмашылық анықталған, яғни бұл үш қой тұқымы фенотиптік тұрғыдан ұқсас болса да, әртүрлі генетикалық шығу тегіне ие және тәуелсіз эволюциялық жолдардан өткен.
Genome-Wide Association Studies (GWAS) Полногеномные ассоциативные исследования (GWAS) Геномдық ассоциациялық зерттеулер (GWAS)
In recent years, genome-wide association studies (GWAS) have become widely used in sheep farming. Akhatayeva et al. (2025) conducted a GWAS study on Kazakh fat-tailed coarse-wool sheep to identify genetic variants associated with body conformation traits [2]. The study analyzed associations with 12 morphometric parameters including live weight, height at withers, height at rump, chest width, chest depth, chest girth, body length, pelvis width, cannon bone circumference, tail width, tail length, and tail weight.
The study identified 25 genome-wide significant single nucleotide polymorphisms (SNPs) associated with various body measurements. These SNPs are located on different chromosomes and are linked to genes involved in skeletal development, muscle growth, and metabolic regulation. Candidate genes identified include MSTN, NCAPG, LCORL, HMGA2, and others known for their role in controlling growth and development in mammals.
В последние годы полногеномные ассоциативные исследования (GWAS) получили широкое распространение в овцеводстве. Ахатаева и соавторы (2025) провели GWAS-исследование казахских курдючных грубошерстных овец для выявления генетических вариантов, связанных с признаками телосложения [2]. В исследовании проанализированы ассоциации с 12 морфометрическими параметрами, включая живую массу, высоту в холке, высоту в крестце, ширину груди, глубину груди, обхват груди, длину туловища, ширину таза, обхват пясти, ширину курдюка, длину курдюка и массу курдюка.
В исследовании выявлено 25 полногеномно значимых однонуклеотидных полиморфизмов (SNP), ассоциированных с различными показателями телосложения. Эти SNP расположены на разных хромосомах и связаны с генами, участвующими в развитии скелета, росте мышц и регуляции метаболизма. Среди идентифицированных генов-кандидатов: MSTN, NCAPG, LCORL, HMGA2 и другие, известные своей ролью в контроле роста и развития у млекопитающих.
Соңғы жылдары геномдық ассоциациялық зерттеу (GWAS) жұмыстары қой шаруашылығында кеңінен қолдана бастады. Геномдық ассоциациялық зерттеу бойынша Ахатаева және басқа авторлары (2025) қазақтың құйрықты қылшық жүнді қойларының дене құрылысы белгілерімен байланысты генетикалық нұсқаларды анықтау үшін зерттеу жүргізді [2]. Зерттеуде тірілей салмағы, шоқтық биіктігі, құйымшақ биіктігі, кеуде ені, кеуде тереңдігі, кеуде айналымы, дене ұзындығы, жамбас ені, асық айналымы, құйрық ені, құйрық ұзындығы және құйрық салмағын қоса алғанда 12 морфометриялық параметрлермен байланыстар талданды.
Зерттеуде дене өлшемдерінің әртүрлі көрсеткіштерімен байланысты 25 геном бойынша маңызды бірнуклеотидті полиморфизм (SNP) анықталды. Бұл SNP-лер әртүрлі хромосомаларда орналасқан және қаңқаның дамуына, бұлшықеттердің өсуіне және метаболизмді реттеуге қатысатын гендермен байланысты. Анықталған кандидат гендер арасында MSTN, NCAPG, LCORL, HMGA2 және сүтқоректілердің өсуі мен дамуын бақылаудағы рөлі белгілі басқа гендер бар.
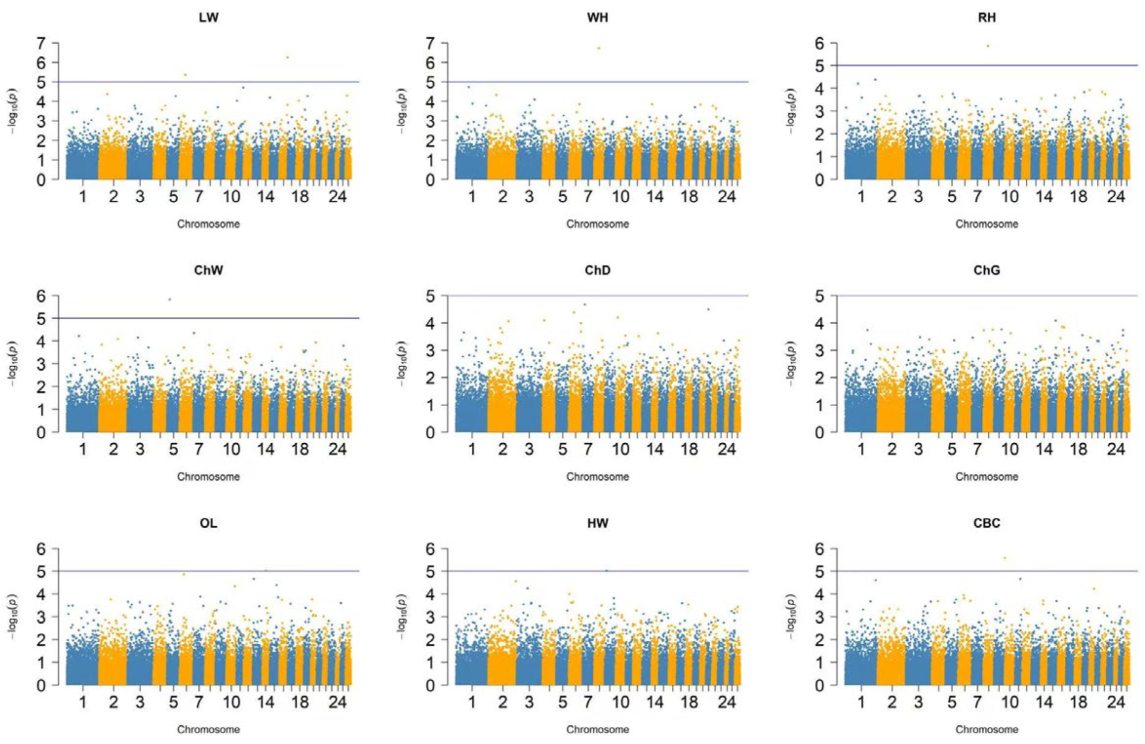
GWAS Manhattan plots for 12 body conformation traits in Kazakh fat-tailed coarse-wool sheep. Each point represents a SNP, with the y-axis showing -log10(p-value) and the x-axis showing chromosome position. The horizontal line indicates the genome-wide significance threshold. Манхэттенские графики GWAS для 12 признаков телосложения казахских курдючных грубошерстных овец. Каждая точка представляет SNP, по оси y показано -log10(p-значение), по оси x - позиция на хромосоме. Горизонтальная линия указывает порог полногеномной значимости. Қазақтың құйрықты қылшық жүнді қойларының 12 дене құрылысы белгілері үшін GWAS Манхэттен графиктері. Әрбір нүкте SNP-ні білдіреді, y осі -log10(p-мәні) көрсетеді, х осі хромосомадағы орынды көрсетеді. Көлденең сызық геном бойынша маңыздылық шегін көрсетеді.
Runs of Homozygosity (ROH) Analysis Анализ гомозиготных участков (ROH) Гомозиготалылық аймақтарын (ROH) талдау
Kozhakhmet et al. (2025) used Runs of Homozygosity (ROH) analysis to assess the level of genetic diversity, relatedness, and identify selection signatures in the aforementioned sheep breed [3]. ROH are continuous stretches of homozygous genotypes in the genome that indicate regions where an individual inherited identical DNA segments from both parents.
The study found that short ROH segments (1-2 Mb) predominate, indicating ancient inbreeding that occurred many generations ago. The genomic inbreeding coefficient based on ROH (FROH) was 0.047, suggesting a moderate level of inbreeding in the population. Analysis of ROH distribution across the genome revealed several genomic regions with high ROH frequency, potentially indicating selection signatures.
These results can be applied in breeding programs and genetic diversity monitoring in sheep farms across the country. The identified ROH-concentrated regions and candidate genes provide important information for developing genomic selection strategies.
Кожахмет и соавторы (2025) использовали анализ гомозиготных участков (ROH) для оценки уровня генетического разнообразия, родственности и выявления следов селекции в вышеупомянутой породе овец [3]. ROH представляют собой непрерывные участки гомозиготных генотипов в геноме, которые указывают на регионы, где особь унаследовала идентичные сегменты ДНК от обоих родителей.
Исследование показало, что преобладают короткие сегменты ROH (1-2 Мб), что указывает на древний инбридинг, произошедший много поколений назад. Геномный коэффициент инбридинга на основе ROH (FROH) составил 0,047, что свидетельствует об умеренном уровне инбридинга в популяции. Анализ распределения ROH по геному выявил несколько геномных регионов с высокой частотой ROH, потенциально указывающих на следы селекции.
Эти результаты могут быть применены в программах разведения и мониторинге генетического разнообразия в овцеводческих хозяйствах по всей стране. Выявленные ROH-концентрированные регионы и гены-кандидаты предоставляют важную информацию для разработки стратегий геномной селекции.
Қожахмет және басқа авторлар (2025) жоғарыда аталған қой тұқымының генетикалық әртүрлілік деңгейін, туыстық қатынасты бағалау және селекция белгілерін анықтау үшін гомозиготалылық (Runs of Homozygosity, ROH) аймақтарын талдауды қолданды [3]. ROH – бұл геномдағы гомозиготалы генотиптердің үздіксіз учаскелері, олар даралардың екі ата-анасынан да бірдей ДНК сегменттерін мұраға алған аймақтарды көрсетеді.
Зерттеу қысқа ROH сегменттері (1-2 Мб) басым екенін көрсетті, бұл көп ұрпақ бұрын болған көне инбридингті көрсетеді. ROH негізіндегі геномдық инбридинг коэффициенті (FROH) 0,047 құрады, бұл популяциядағы инбридинг деңгейінің орташа екенін көрсетеді. ROH-тың геном бойынша таралуын талдау ROH жиілігі жоғары бірнеше геномдық аймақтарды анықтады, бұл селекция белгілерін көрсетуі мүмкін.
Бұл алынған нәтижелер елдегі қой шаруашылықтарында асылдандыру бағдарламалары мен генетикалық әртүрлілікті бақылау мақсатында қолдануға болады. Анықталған ROH шоғырланған аймақтар мен кандидат гендер геномдық селекция стратегияларын әзірлеу үшін маңызды ақпарат береді.
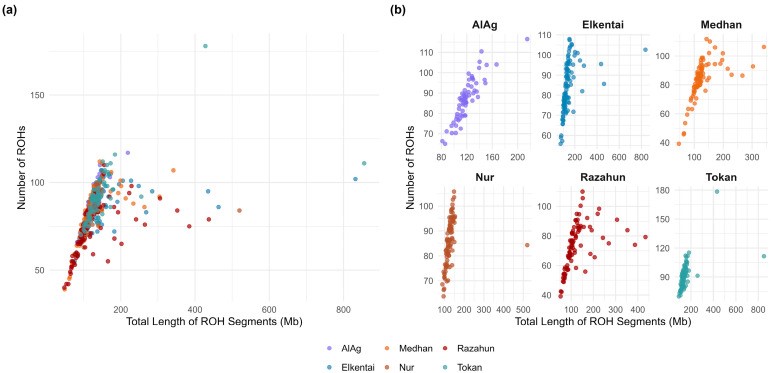
(a) Scatter plot showing the number of ROH segments and their total length for all 497 individuals. (b) Manhattan plot showing ROH frequency distribution across the genome, with peaks indicating regions of high homozygosity potentially under selection. (a) Диаграмма рассеяния, показывающая количество сегментов ROH и их общую длину для всех 497 особей. (b) Манхэттенский график, показывающий распределение частоты ROH по геному, где пики указывают на регионы высокой гомозиготности, потенциально находящиеся под селекцией. (a) Барлық 497 дара үшін ROH сегменттерінің саны мен жалпы ұзындығын көрсететін шашыраңқы диаграмма. (b) Геном бойынша ROH жиілігінің таралуын көрсететін Манхэттен графигі, шыңдар селекция астында болуы мүмкін жоғары гомозиготалылық аймақтарын көрсетеді.
Khamzina et al. (2025) conducted research on meat and wool productivity traits by studying homozygosity regions in 5 local sheep breeds in Kazakhstan [4]. The study included Edilbay (ED, n=10), Kazakh fine-wool (KF, n=10), Kazakh coarse-wool (KC, n=10), Semirechensk (SR, n=9), and Kazakh fat-tailed coarse-wool (KFC, n=497) breeds.
The data obtained show that the Kazakh fine-wool and Edilbay breeds have low genomic inbreeding levels (FROH = 0.039 and 0.037). This indicates limited consanguineous mating in these breeds. However, relatively higher FROH values were recorded for Semirechensk (0.075), Kazakh coarse-wool (0.063), and Kazakh fat-tailed coarse-wool (0.047) breeds.
Хамзина и соавторы (2025) провели исследование признаков мясной и шерстной продуктивности путем изучения гомозиготных регионов у 5 местных пород овец в Казахстане [4]. В исследование были включены породы эдильбай (ED, n=10), казахская тонкорунная (KF, n=10), казахская грубошерстная (KC, n=10), семиреченская (SR, n=9) и казахская курдючная грубошерстная (KFC, n=497).
Полученные данные показывают, что казахская тонкорунная и эдильбаевская породы имеют низкие уровни геномного инбридинга (FROH = 0,039 и 0,037). Это указывает на ограниченное родственное спаривание в этих породах. Однако относительно более высокие значения FROH были зафиксированы для семиреченской (0,075), казахской грубошерстной (0,063) и казахской курдючной грубошерстной (0,047) пород.
Хамзина және басқа авторлар (2025) қазақстандағы жергілікті 5 қой тұқымдарына гомозиготалық аймақтарды зерттеу арқылы ет және жүн өнімділігіне қатысты зерттеу жүргізген [4]. Зерттеуде Еділбай (ED, n=10), қазақтың биязы жүнді (KF, n=10), қазақтың қылшық жүнді (KC, n=10), жетісу (SR, n=9) және қазақтың құйрықты қылшық жүнді (KFC, n=497) тұқымдары қамтылды.
Алынған деректер қазақтың биязы жүнді және еділбай тұқымдарында геномдық инбридинг деңгейінің төмен екенін көрсетеді (FROH = 0,039 және 0,037). Бұл аталған тұқымдарда туыстас шағылыстырудың шектеулі болғанын көрсетеді. Алайда, жетісу (0,075), қазақтың қылшық жүнді (0,063) және қазақтың құйрықты қылшық жүнді (0,047) тұқымдары үшін салыстырмалы түрде жоғарырақ FROH мәндері тіркелді.
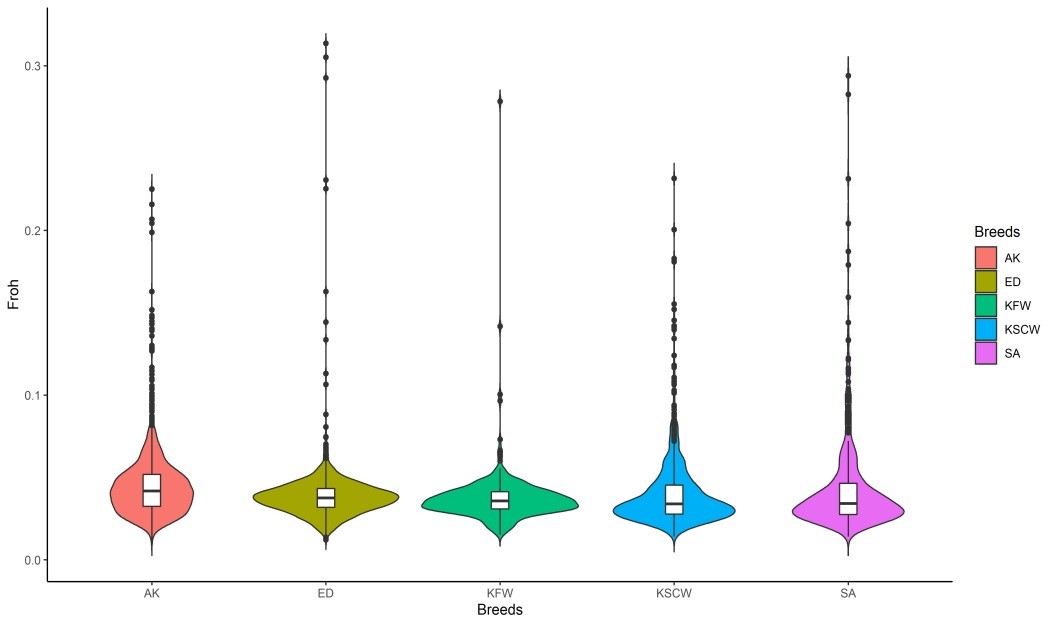
Comparison of genomic inbreeding coefficients (FROH) across five Kazakh sheep breeds. Lower values indicate higher genetic diversity and less inbreeding, while higher values suggest more intensive breeding practices. Сравнение геномных коэффициентов инбридинга (FROH) по пяти казахским породам овец. Более низкие значения указывают на большее генетическое разнообразие и меньший инбридинг, в то время как более высокие значения свидетельствуют о более интенсивных практиках разведения. Бес қазақ қой тұқымы бойынша геномдық инбридинг коэффициенттерінің (FROH) салыстырмасы. Төмен мәндер жоғары генетикалық әртүрлілікті және аз инбридингті көрсетеді, ал жоғары мәндер қарқынды асылдандыру практикасын көрсетеді.
Nevertheless, the indicators are not excessively high, which suggests that genetic diversity has not been completely lost in these breeds, and further selective work can be effectively conducted through inbreeding management to improve productive traits. Identified candidate genes in ROH regions include genes associated with meat productivity (MSTN, GDF8), wool quality (FGF5, PDGFD), and adaptation to environmental conditions (TSHR, KITLG).
Тем не менее, показатели не являются чрезмерно высокими, что свидетельствует о том, что генетическое разнообразие не было полностью утрачено в этих породах, и дальнейшая селекционная работа может эффективно проводиться через управление инбридингом для улучшения продуктивных признаков. Идентифицированные гены-кандидаты в регионах ROH включают гены, связанные с мясной продуктивностью (MSTN, GDF8), качеством шерсти (FGF5, PDGFD) и адаптацией к условиям окружающей среды (TSHR, KITLG).
Соған қарамастан, көрсеткіштердің шамадан тыс жоғары болмауы бұл тұқымдарда генетикалық әртүрліліктің толық жоғалмағанын және инбридингті басқару арқылы селекциялық жұмыстарды әрі қарай тиімді жүргізу мүмкін екенін көрсетеді. ROH аймақтарындағы анықталған кандидат гендер ет өнімділігімен (MSTN, GDF8), жүн сапасымен (FGF5, PDGFD) және қоршаған орта жағдайларына бейімделумен (TSHR, KITLG) байланысты гендерді қамтиды.
Goat Genetic Research Генетические исследования коз Ешкілердің генетикалық зерттеулері
Kichamu et al. (2025) conducted research to understand the genetic structure of local goat populations in Kazakhstan [5]. The study used 120 samples from six regions and analyzed 778,044 SNPs. Samples were collected from six settlements: Ushterek (Kostanay region), Kosseit (Kyzylorda region), Shokpar and Kundyzdy (Turkestan region), and Darbaza (Zhetysu region).
Analysis revealed significant variation in genetic diversity between different populations. For example, samples from Shokpar and Kundyzdy settlements showed predominant excess heterozygosity, while samples from Kosseit and Darbaza settlements had high inbreeding levels. Ushterek settlement samples showed a balanced genetic structure with moderate diversity.
Кичаму и соавторы (2025) провели исследование для понимания генетической структуры местных популяций коз в Казахстане [5]. В исследовании использовались 120 образцов из шести регионов и анализировались 778 044 SNP. Образцы были собраны из шести населенных пунктов: Үштерек (Костанайская область), Қосейіт (Кызылординская область), Шоқпар и Құндызды (Туркестанская область) и Дарбаза (Жетысуская область).
Анализ выявил значительную вариацию генетического разнообразия между различными популяциями. Например, образцы из населенных пунктов Шоқпар и Құндызды показали преобладающую избыточную гетерозиготность, в то время как образцы из Қосейіт и Дарбаза имели высокие уровни инбридинга. Образцы из населенного пункта Үштерек показали сбалансированную генетическую структуру с умеренным разнообразием.
Kichamu және басқалары (2025) қазақстанның жергілікті ешкі популяцияларының генетикалық құрылымын түсіну мақсатында зерттеулер жүргізді [5]. Зерттеуде алты аймақтан алынған 120 үлгі қолданылған және 778 044 SNP талданған. Үлгілер алты елді мекеннен жиналды: Үштерек (Қостанай облысы), Қосейіт (Қызылорда облысы), Шоқпар және Құндызды (Түркістан облысы) және Дарбаза (Жетісу облысы).
Талдау әртүрлі популяциялар арасындағы генетикалық әртүрліліктің айтарлықтай өзгергіштігін анықтады. Мысалы, Шоқпар және Құндызды елді мекендері үлгілерінде шамадан тыс гетерозиготалылық басым болса, ал Қосейіт пен Дарбаза елді мекен үлгілерінде инбридинг деңгейі жоғары болған. Үштерек елді мекені үлгілері орташа әртүрлілікпен теңдестірілген генетикалық құрылымды көрсетті.
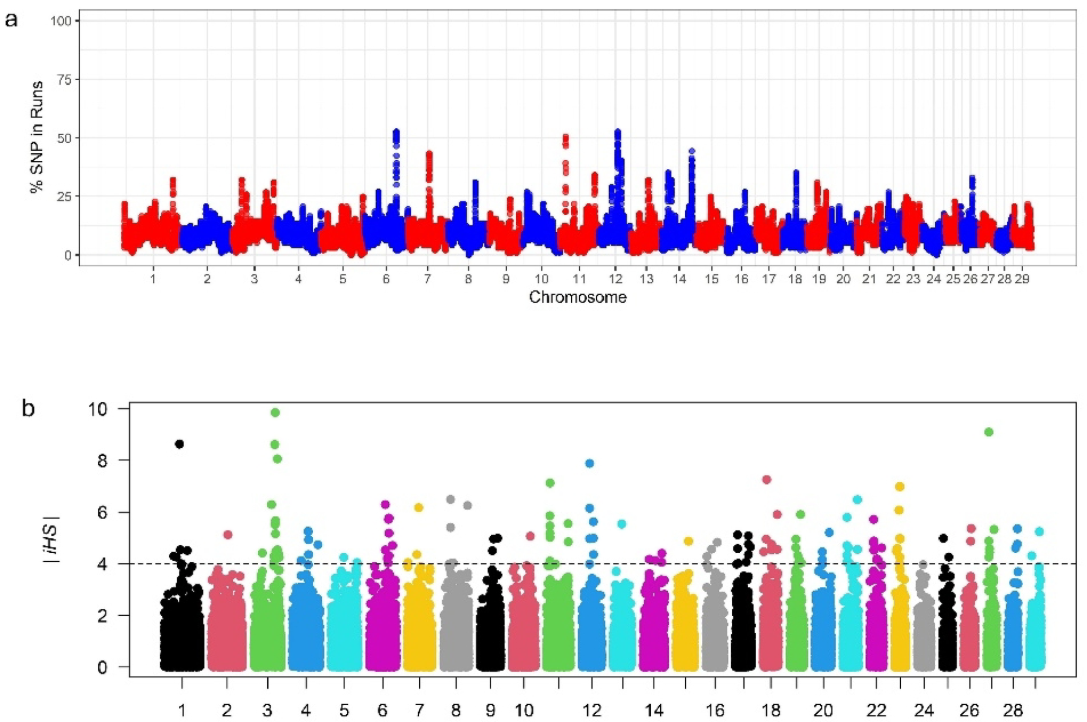
Manhattan plots showing (a) percentage of SNPs per chromosome and (b) distribution of integrated haplotype score (iHS) across chromosomes. Peaks indicate regions under positive selection in Kazakhstan local goat populations. Манхэттенские графики, показывающие (a) процент SNP на хромосому и (b) распределение интегрированного гаплотипного балла (iHS) по хромосомам. Пики указывают на регионы под положительной селекцией в местных популяциях коз Казахстана. Манхэттен графиктері (а) хромосома үшін SNP пайызын және (b) хромосомалар бойынша біріктірілген гаплотип ұпайының (iHS) таралуын көрсетеді. Шыңдар Қазақстанның жергілікті ешкі популяцияларындағы оң селекция астындағы аймақтарды көрсетеді.
II. Genetic Research on Cattle ІІ. Генетические исследования крупного рогатого скота ІІ. Ірі қара мал шаруашылығындағы генетикалық зерттеулер
Cattle farming occupies a leading position in Kazakhstan's agro-industrial complex and plays an important role in forming the country's food security and export potential. The Kazakh Whiteheaded cattle breed is one of the main beef breeds raised in the country and is characterized by high adaptive qualities to continental climate conditions.
As an example of ongoing work in this direction, the research by Khamzina et al. (2025) can be mentioned [6]. This study examined the genetic structure and ancestral breed composition of Kazakh Whiteheaded cattle using whole-genome resequencing. The research revealed that the Kazakh Whiteheaded cattle genome consists of genetic contributions from three breeds: Hereford (45%), Altai (30%), and Kalmyk (25%).
Скотоводство занимает ведущее место в агропромышленном комплексе Казахстана и играет важную роль в формировании продовольственной безопасности и экспортного потенциала страны. Казахская белоголовая порода крупного рогатого скота является одной из основных мясных пород, разводимых в стране, и характеризуется высокими адаптивными качествами к условиям континентального климата.
В качестве примера проводимых работ в этом направлении можно привести исследование Хамзиной и соавторов (2025) [6]. В этом исследовании изучалась генетическая структура и состав предковых пород казахской белоголовой породы крупного рогатого скота с использованием полногеномного ресеквенирования. Исследование выявило, что геном казахской белоголовой породы крупного рогатого скота состоит из генетического вклада трех пород: герефорд (45%), алтайская (30%) и калмыцкая (25%).
Ірі қара мал шаруашылығы Қазақстанның агроөнеркәсіптік кешенінде жетекші орын алады және елдің азық-түлік қауіпсіздігі мен экспорттық әлеуетін қалыптастыруда маңызды рөл атқарады. Қазақтың ақбас сиыры елде өсірілетін негізгі етті тұқымдардың бірі болып табылады және континенталды климат жағдайларына жоғары бейімделу қасиеттерімен сипатталады.
Осындай бағытта жүргізіліп жатқан жұмыстардың бірі ретінде Хамзина және басқа авторлардың (2025) еңбегін айтуға болады [6]. Бұл зерттеу жұмысында қазақтың ақбас ірі қара мал тұқымының генетикалық құрылымы мен ата-бабалық тұқымдар құрамы толық геномды қайта секвенирлеу арқылы зерттелген. Зерттеу қазақтың ақбас ірі қара мал тұқымының геномы үш тұқымның генетикалық үлесінен тұратынын анықтады: герефорд (45%), алтай (30%) және қалмақ (25%).

Selection signatures identified in the genome of Kazakh Whiteheaded cattle showing regions under positive selection. Yakut cattle were used as an outgroup for comparison, helping to identify breed-specific selection signatures. Следы селекции, идентифицированные в геноме казахской белоголовой породы крупного рогатого скота, показывающие регионы под положительной селекцией. Якутский скот был использован в качестве внешней группы для сравнения, помогая идентифицировать породоспецифичные следы селекции. Қазақтың ақбас ірі қара мал геномында анықталған сұрыптау белгілері оң селекция астындағы аймақтарды көрсетеді. Якут ірі қара малдары салыстыру үшін сыртқы топ ретінде пайдаланылды, бұл тұқымға тән сұрыптау белгілерін анықтауға көмектесті.
Through principal component analysis (PCA) and ancestry determination, the Kazakh Whiteheaded cattle genome showed 45% similarity with Hereford, 30% with Altai, and 25% with Kalmyk breeds. Additionally, genomic analysis revealed significant selection signatures in genes associated with meat productivity, adaptation to climate conditions, and disease resistance. These findings provide important information for developing genomic selection programs for Kazakh Whiteheaded cattle.
The next study was conducted by Niyazbekova et al. (2025) [7] and aimed to characterize the genetic composition and origins of cattle breeds in Kazakhstan. The authors performed whole-genome sequencing of 100 samples from six different Kazakhstani cattle populations, achieving an average sequencing depth of 30x.
С помощью анализа главных компонент (PCA) и определения происхождения геном казахской белоголовой породы крупного рогатого скота показал 45% сходства с герефордской, 30% с алтайской и 25% с калмыцкой породами. Кроме того, геномный анализ выявил значительные следы селекции в генах, связанных с мясной продуктивностью, адаптацией к климатическим условиям и устойчивостью к болезням. Эти находки предоставляют важную информацию для разработки программ геномной селекции казахской белоголовой породы крупного рогатого скота.
Следующее исследование было проведено Ниязбековой и соавторами (2025) [7] и было направлено на характеристику генетического состава и происхождения пород крупного рогатого скота в Казахстане. Авторы выполнили полногеномное секвенирование 100 образцов из шести различных казахстанских популяций крупного рогатого скота, достигнув средней глубины секвенирования 30x.
Негізгі компоненттік талдау (РСА) және ата-тегін анықтау арқылы қазақтың ақбас ірі қара мал тұқымы геномында 45% герефорд, 30% алтай және 25% қалмақ тұқымдарымен ұқсастық табылған. Сонымен қатар, геномдық талдау ет өнімділігімен, климаттық жағдайларға бейімделумен және аурулардың қарсылығымен байланысты гендерде айтарлықтай сұрыптау белгілерін анықтады. Бұл нәтижелер қазақтың ақбас ірі қара мал тұқымы үшін геномдық селекция бағдарламаларын әзірлеу үшін маңызды ақпарат береді.
Келесі жұмыс Ниязбекова және басқа авторлардың (2025) жүргізген [7] және ол Қазақстандағы ірі қара мал тұқымдарының генетикалық құрамын және шығу тектеріне сипаттама беру мақсатында орындалған. Авторлар алты әртүрлі қазақстандық ірі қара мал популяцияларынан 100 үлгінің толық геномды секвенирлеуін орындап, орташа секвенирлеу тереңдігі 30x-қа жетті.
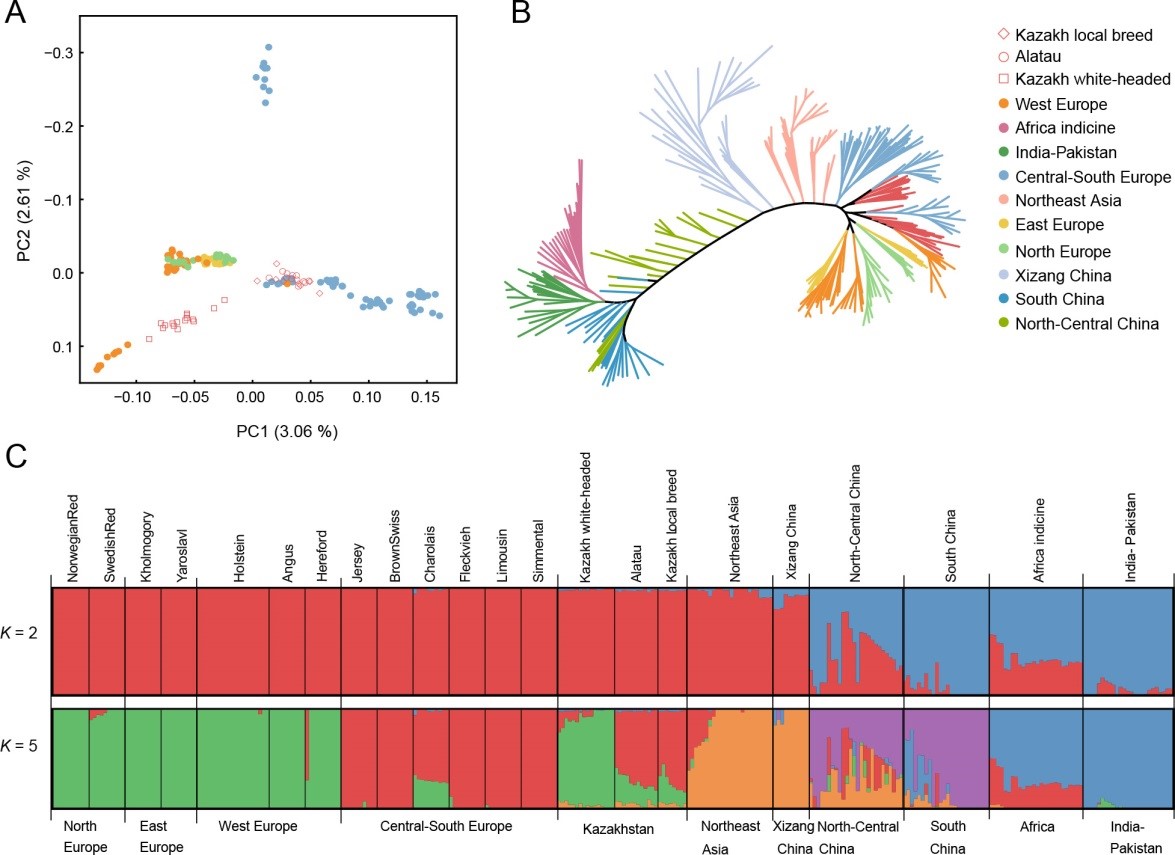
A: Principal Component Analysis of taurine cattle from various geographical regions. B: Phylogenetic tree based on genome-wide SNP data. The analysis reveals the complex genetic history of Kazakhstani cattle populations and their relationships with other Eurasian breeds. A: Анализ главных компонент тауринного скота из различных географических регионов. B: Филогенетическое дерево на основе полногеномных SNP-данных. Анализ раскрывает сложную генетическую историю казахстанских популяций крупного рогатого скота и их взаимосвязи с другими евразийскими породами. A: Әртүрлі географиялық аймақтардан алынған таурин ірі қара малының негізгі компоненттік талдауы. B: Геном бойынша SNP деректеріне негізделген филогенетикалық ағаш. Талдау қазақстандық ірі қара мал популяцияларының күрделі генетикалық тарихын және олардың басқа еуразиялық тұқымдармен байланысын ашады.
As a result, the East Asian taurine lineage may represent the initial genetic contribution to Kazakhstani cattle, but was subsequently displaced through migration of Eurasian cattle, which explains the current genetic structure of Kazakhstani cattle populations. The study identified several genomic regions under selection related to adaptation to harsh climatic conditions, disease resistance, and productivity traits.
В результате восточноазиатская тауринная линия может представлять первоначальный генетический вклад в казахстанский крупный рогатый скот, но впоследствии была вытеснена за счет миграции евразийского скота, что объясняет нынешнюю генетическую структуру казахстанских популяций крупного рогатого скота. В исследовании выявлено несколько геномных регионов под селекцией, связанных с адаптацией к суровым климатическим условиям, устойчивостью к болезням и признаками продуктивности.
Нәтижесінде, Шығыс азиялық таурин линиясы қазақтың ірі қара малының алғашқы генетикалық үлесін білдіруі мүмкін, алайда соңынан Еуразия ірі қара малдардың миграциясы арқылы ығыстырылды, бұл қазіргі ірі қара мал популяцияларының генетикалық құрылымын түсіндіреді. Зерттеуде қатал климаттық жағдайларға бейімделу, аурулардың қарсылығы және өнімділік белгілерімен байланысты селекция астында бірнеше геномдық аймақтар анықталды.
Conclusions Выводы Қорытынды
This review article, based on scientific publications on genetic research of sheep, goats, and cattle breeds published in 2025, examines the current state and development trends in this field. The analyzed studies demonstrate significant progress in understanding the genetic architecture, population structure, and adaptive characteristics of Kazakhstani livestock breeds.
Thus, scientific articles on sheep, goat, and cattle genetics published in 2025 are important not only for Kazakhstan's livestock industry but also for global genetics and breeding science. The obtained results form a solid foundation for developing modern breeding programs based on genomic technologies and contribute to preserving the genetic diversity of valuable local breeds adapted to harsh continental climate conditions.
В данной обзорной статье, основанной на научных публикациях по генетическим исследованиям пород овец, коз и крупного рогатого скота, опубликованных в 2025 году, рассмотрено современное состояние и тенденции развития в этой области. Проанализированные исследования демонстрируют значительный прогресс в понимании генетической архитектуры, популяционной структуры и адаптивных характеристик казахстанских пород сельскохозяйственных животных.
Таким образом, научные статьи по генетике овец, коз и крупного рогатого скота, опубликованные в 2025 году, имеют важное значение не только для животноводства Казахстана, но и для мировой науки о генетике и селекции. Полученные результаты формируют прочную основу для разработки современных программ разведения на основе геномных технологий и способствуют сохранению генетического разнообразия ценных местных пород, адаптированных к суровым условиям континентального климата.
Бұл шолу мақалада 2025 жылы жарияланған қой-ешкі және ірі қара мал тұқымдарының генетикалық зерттеулері негізінде жарыққа шыққан ғылыми еңбектерге сүйене отырып, аталған бағыттың қазіргі жағдайы мен даму үрдістері қарастырылды. Талданған зерттеулер Қазақстандағы ауыл шаруашылық мал тұқымдарының генетикалық архитектурасын, популяциялық құрылымын және бейімделу сипаттамаларын түсінуде айтарлықтай прогреске жетілгенін көрсетеді.
Сонымен, 2025 жылы жарыққа шыққан қой-ешкі және ірі қара малдардың генетикасына байланысты ғылыми мақалалар Қазақстанның мал шаруашылығы үшін ғана емес, сондай-ақ жаһандық генетика мен селекция ғылымы үшін де маңызды. Алынған нәтижелер геномдық технологияларға негізделген қазіргі заманғы селекциялық бағдарламаларды әзірлеу үшін берік негіз құрайды және континенталды климаттың қатал жағдайларына бейімделген құнды жергілікті тұқымдардың генетикалық әртүрлілігін сақтауға ықпал етеді.
Future Research Directions and Recommendations Направления будущих исследований и рекомендации Болашақ зерттеу бағыттары және ұсынымдар
While the review of genetic research on sheep/goat and cattle breeds in Kazakhstan shows significant scientific progress, there are several methodological, infrastructural, and organizational issues that need to be addressed in this field. The following priority areas for further research and practical implementation can be identified:
- Expansion of genomic databases: Creating a unified national genomic database for all major livestock breeds in Kazakhstan, standardizing phenotypic and genotypic data collection protocols.
- Development of genomic selection programs: Implementing genomic prediction methods for economically important traits, training specialists in genomic technologies.
- Study of adaptation mechanisms: Detailed investigation of genetic mechanisms of adaptation to climate change, research on disease resistance genes and development of genetic markers.
- International collaboration: Participation in international genomic research consortia, exchange of genetic material and data with foreign scientific centers.
- Infrastructure development: Creating modern genotyping and sequencing centers, establishing cryobanks for genetic resources.
- Regulatory framework: Developing regulations for genomic selection use in breeding, establishing standards for genetic material quality and certification.
Хотя обзор генетических исследований пород овец/коз и крупного рогатого скота в Казахстане показывает значительный научный прогресс, существует ряд методологических, инфраструктурных и организационных вопросов, которые необходимо решить в этой области. Можно выделить следующие приоритетные направления дальнейших исследований и практического внедрения:
- Расширение геномных баз данных: Создание единой национальной геномной базы данных для всех основных пород сельскохозяйственных животных в Казахстане, стандартизация протоколов сбора фенотипических и генотипических данных.
- Разработка программ геномной селекции: Внедрение методов геномного прогнозирования для хозяйственно важных признаков, обучение специалистов геномным технологиям.
- Изучение механизмов адаптации: Детальное исследование генетических механизмов адаптации к изменению климата, исследование генов устойчивости к болезням и разработка генетических маркеров.
- Международное сотрудничество: Участие в международных геномных исследовательских консорциумах, обмен генетическим материалом и данными с зарубежными научными центрами.
- Развитие инфраструктуры: Создание современных центров генотипирования и секвенирования, создание криобанков генетических ресурсов.
- Нормативно-правовая база: Разработка регламентов использования геномной селекции в разведении, установление стандартов качества и сертификации генетического материала.
Қазақстандағы қой/ешкі және ірі қара мал тұқымдарының генетикалық зерттеулеріне жүргізілген шолу елеулі ғылыми ілгерілеудің болғанын көрсеткенімен, бұл салада шешілуі тиіс бірқатар әдістемелік, инфрақұрылымдық және ұйымдастырушылық мәселелер бар. Одан әрі зерттеулер мен практикалық енгізудің келесі басым бағыттарын анықтауға болады:
- Геномдық дерекқорларды кеңейту: Қазақстандағы барлық негізгі ауыл шаруашылық мал тұқымдары үшін бірыңғай ұлттық геномдық дерекқорды құру, фенотиптік және генотиптік деректерді жинау хаттамаларын стандарттау.
- Геномдық селекция бағдарламаларын әзірлеу: Шаруашылық маңызды белгілер үшін геномдық болжау әдістерін енгізу, мамандарды геномдық технологияларға оқыту.
- Бейімделу механизмдерін зерттеу: Климат өзгеруіне бейімделудің генетикалық механизмдерін егжей-тегжейлі зерттеу, аурулардың қарсылық гендерін зерттеу және генетикалық маркерлерді әзірлеу.
- Халықаралық ынтымақтастық: Халықаралық геномдық зерттеу консорциумдарына қатысу, шетелдік ғылыми орталықтармен генетикалық материалдармен және деректермен алмасу.
- Инфрақұрылымды дамыту: Заманауи генотиптеу және секвенирлеу орталықтарын құру, генетикалық ресурстардың криобанктерін құру.
- Нормативтік-құқықтық база: Асылдандыруда геномдық селекцияны пайдалану регламенттерін әзірлеу, генетикалық материалдың сапасы мен сертификаттау стандарттарын белгілеу.
References Литература Әдебиеттер
- Dossybayev K., et al. Genome-Wide SNP Analysis Reveals the Unique Genetic Characteristics of Kazakh Fat-Tailed Coarse-Wooled Sheep. Biology. 2025;14(11):1478. https://doi.org/10.3390/biology14111478
- Akhatayeva Z, Dossybayev K, Kozhakhmet A, Yermekova M, Kapassuly T, Yergali K, Kulboldin T, Torekhanov A, Kulataev B, Iskakov K, et al. Genome-Wide Association Study for Body Conformation Traits in Kazakh Fat-Tailed Coarse-Wool Sheep. Genes. 2025; 16(9):1023. https://doi.org/10.3390/genes16091023
- Kozhakhmet A, Akhatayeva Z, Dossybayev K, Yermekova M, Kapassuly T, Yergali K, Torekhanov A, Bissenov U, Lan X, Kulataev B. Genomic Characterization of the Kazakh Fat-Tailed Coarse-Wool Sheep Breed Using ROH Analysis. Animals (Basel). 2025 Sep 16;15(18):2714. doi: 10.3390/ani15182714
- Khamzina A., Smagulov D., Dossybayev K., Kantanen J., Khamzin K. Assessing runs of homozygosity reveals production traits of Kazakh sheep breeds. Brazilian Journal of Biology, 85:2025. https://doi.org/10.1590/1519-6984.292980
- Kichamu N., Wanjala G., Dossybayev K., Bagi Z., Bekmanov B., Kusza S. Genome-wide analysis provides insight into the genetic diversity and adaptability of Kazakhstan local goats. Sci Rep 15, 19327 (2025). https://doi.org/10.1038/s41598-025-02427-8
- Khamzina AK, Igoshin AV, Muslimova ZU, Turgumbekov AA, Khussainov DM, Yudin NS, Ussenbekov YS, Larkin DM. Resequencing Composite Kazakh Whiteheaded Cattle: Insights into Ancestral Breed Contributions, Selection Signatures, and Candidate Genetic Variants. Animals. 2025; 15(3):385. https://doi.org/10.3390/ani15030385
- Zhannur Niyazbekova, Yuan Xu, Min Qiu, Hao-Ping Wang, Ibragimov Primkul, Hojjat Asadollahpour Nanaei, Yessengali Ussenbekov, Kuanysh Kassen, Yi Liu, Cai-Yue Gao, Shynar Akhmetsadykova, Nuriddin Ruzikulov, Yu Jiang, Yu-Dong Cai. 2025. Whole-genome sequencing reveals genetic architecture and selection signatures of Kazakh cattle. Zoological Research, 46(2): 301-311. DOI: 10.24272/j.issn.2095-8137.2024.235